Ejemplo: Correlación 2D y coincidencia de prototipos
Muestra la correlación de un kernel 2D con una imagen en el dominio espacial.
Un kernel interesante es el gaussiano, que produce un efecto de suavizado.
Para obtener información sobre el uso de este ejemplo, consulte Acerca de los ejemplos de procesamiento de imágenes
Correlación 2D
1. Utilice la función READ_IMAGE para leer una imagen.
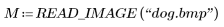
2. Utilice la función WRITEBMP para guardar la imagen en un fichero.
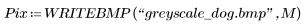
3. Defina el rango y la función del kernel.
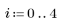
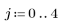
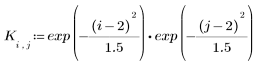
4. Evalúe la matriz 5 x 5 del kernel.
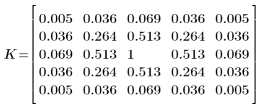
Este kernel es simétrico, por lo que su efecto es el mismo que el de la convolución, equivalente a la correlación con el kernel invertido.
5. Defina un factor de escala mcscale.
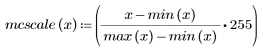
6. Calcule la correlación de la cruz y, a continuación, ajuste el resultado a escala de grises de 8 bits de 0 a 255.
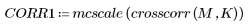
7. Utilice la función WRITEBMP para guardar los resultados en un fichero.
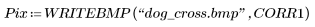
8. Trace la imagen original y la correlación de la imagen con el kernel.
(greyscale_dog.bmp) | (dog_cross.bmp) |
Correlación de prototipos
1. Utilice la función READ_IMAGE para leer una imagen nueva.
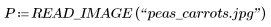
2. Utilice la función WRITEBMP para guardar los resultados en un fichero.
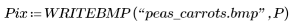
(peas_carrots.bmp)
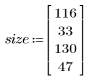
La selección elige como plantilla una zanahoria representativa.
3. Defina la altura y el ancho de la plantilla.
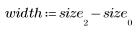
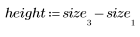
5. Trace la plantilla y las imágenes de zanahorias.
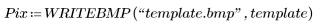
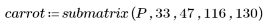
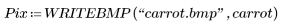
(template.bmp) | (carrot.bmp) |
6. Defina el umbral de correlación.
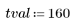
7. Utilice la plantilla uniforme del mismo tamaño que la zanahoria seleccionada o la imagen de zanahoria representativa que haya seleccionado para calcular el número de coincidencias:
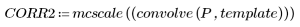
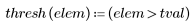
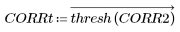
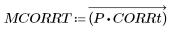
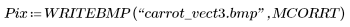
(carrot_vect.bmp) |
Se ha sombreado la mayoría de los guisantes mediante valores no correlativos del umbral, mientras que la mayoría de las zanahorias se encuentran visibles aún. La coincidencia tiene lugar entre la imagen original y la plantilla rectangular de densidad uniforme, que selecciona las zanahorias de una bolsa de verduras congeladas en esta muestra aleatoria.
8. Calcule el porcentaje aproximado de zanahorias que hay en la imagen original.
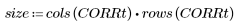
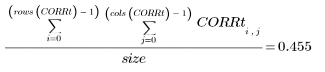
Esta técnica se emplea también para el recuento de bacterias y otra estimación de porcentajes de funcionalidades de la imagen.